近日,上海科技大学生命科学与技术学院孙博课题组在减数分裂同源重组核心机制研究中取得突破性进展,在国际学术期刊《美国国家科学院院刊》(PNAS)上发表了题为“HOP2–MND1 chaperones a diffusing DMC1–ssDNA complex to survey dsDNA for homology recognition during meiotic recombination”的研究论文,在单分子水平揭示减数分裂重组中的特异重组酶DMC1在供体双链DNA上进行一维滑动扫描,并在辅助因子HOP2–MND1复合物的帮助下,精准识别同源序列。
减数分裂是生殖细胞形成的关键过程,其核心环节是分别来自父本和母本的同源染色体间精准配对与交换。在减数分裂早期,为确保遗传信息在配子形成过程中被准确、等量地分配,细胞会主动在基因组中制造双链断裂,随后由重组酶在单链DNA上组装核蛋白复合物,并在庞大而高度压缩的染色质环境中寻找与之完全互补的同源序列。若此过程出错,将导致不孕、流产或唐氏综合征等染色体疾病。RecA家族重组酶DMC1在减数分裂过程中特异表达,其功能的缺失可直接导致遗传信息的不稳定及疾病的发生。然而,DMC1重组酶如何在庞大基因组中高效锁定匹配的同源序列仍悬而未决。
本研究将光镊技术与共聚焦荧光显微技术相结合,在单分子水平实时动态观测DMC1与供体DNA的互作。发现DMC1多聚体可沿双链DNA进行长程滑动,并通过短暂解旋产生局部DNA泡结构,为后续序列比对提供窗口(图1左)。进一步还发现,仅靠DMC1–ssDNA复合物自身难以稳定识别同源序列,而HOP2–MND1的加入可显著提高序列对接概率。HOP2–MND1不依赖其自身的DNA结合能力,而是通过与DMC1相互作用稳定ssDNA–dsDNA交界处,扩大DNA泡窗口,使同源比对更为高效(图1右)。这一结果揭示了DMC1–HOP2–MND1作为减数分裂特化“同源搜索单元”的重要角色。
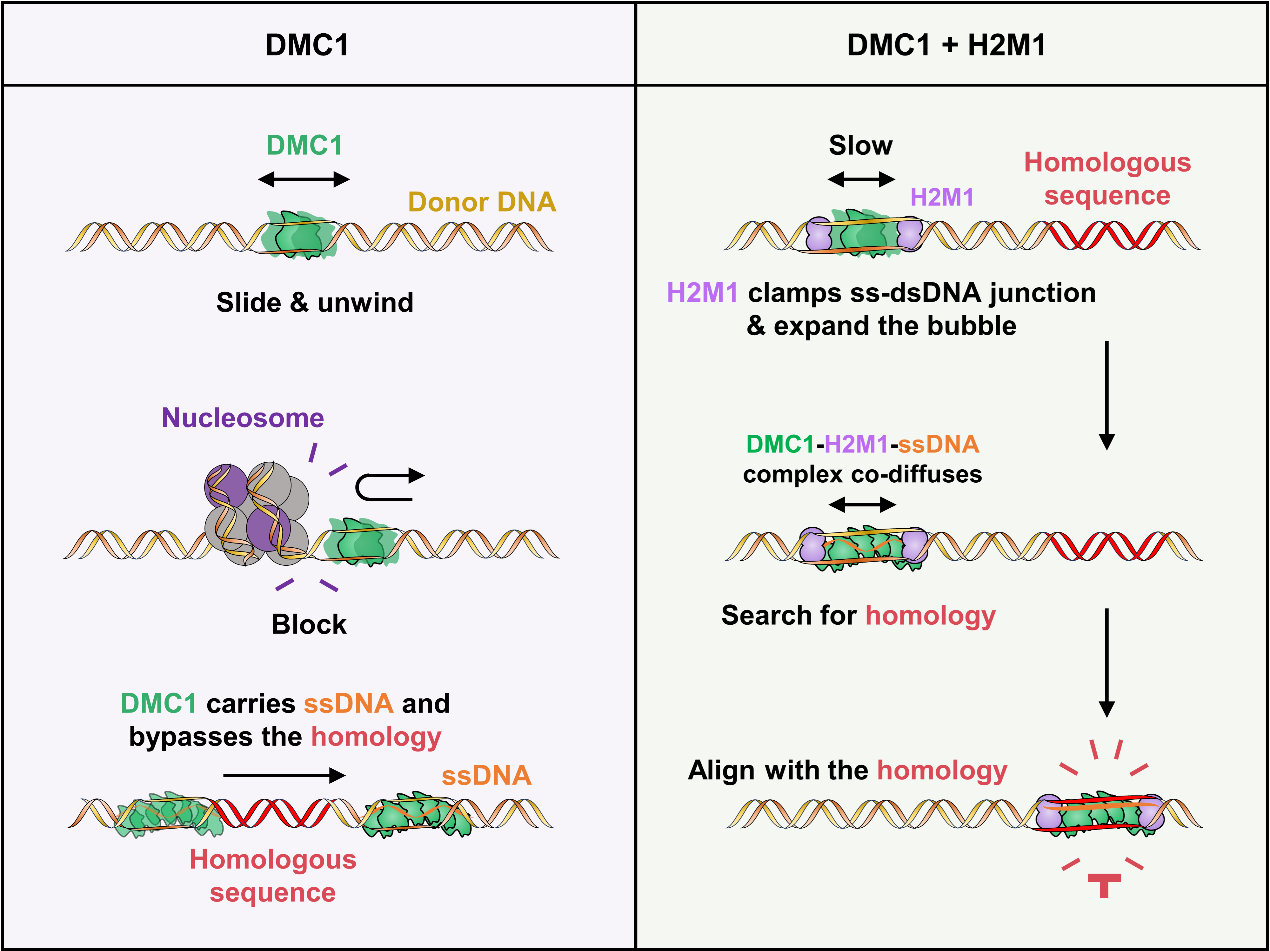
图1:左侧:DMC1沿供体dsDNA滑动并解旋形成动态DNA泡,滑动的DMC1可以携带ssDNA,但无法跨越核小体及识别同源序列。右侧:辅因子HOP2–MND1(H2M1)复合物与DMC1共同滑动并且帮助DMC1生成更大的DNA泡,实现同源序列识别。
该研究首次从单分子角度解析了DMC1搜索同源序列的分子机制,提出了“扩散-夹持”协同新模型,完善了真核生物同源重组理论框架。这一发现阐明了真核生物减数分裂同源配对的分子基础,为理解重组缺陷、染色体非整倍体形成及不孕不育等疾病的分子来源提供了新的视角,也为未来针对重组过程的调控策略提供了潜在方向。
上科大生命学院2024级博士研究生程昺凯为论文第一作者,孙博常任副教授为通讯作者,上海科技大学为论文第一单位。


 沪公网安备 31011502006855号
沪公网安备 31011502006855号